Neues Forschungswerkzeug entschlüsselt, wie Zellen die Proteinproduktion steuern
Emil Schmitt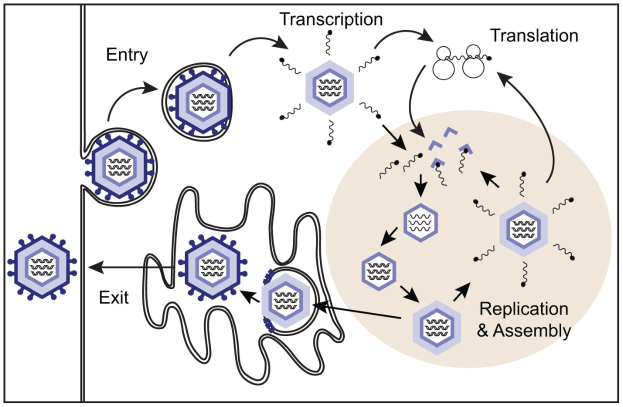
Neues Forschungswerkzeug entschlüsselt, wie Zellen die Proteinproduktion steuern
Ein neues Forschungswerkzeug wurde entwickelt, um genau zu untersuchen, wie Zellen die Proteinproduktion steuern. Der Durchbruch stammt von Wissenschaftler:innen des Universitätsklinikums Bonn (UKB), der Universität Bonn und der Stanford University. Ihre Arbeit bietet eine zuverlässige Methode zur Analyse interner Ribosomen-Eintrittsstellen (IRES), die eine zentrale Rolle bei der Genregulation spielen.
IRES sind spezielle RNA-Sequenzen, die die Proteinsynthese starten können, ohne auf die übliche 5'-Cap-Struktur angewiesen zu sein. Diese Stellen kommen sowohl in viralen als auch in eukaryotischen Genomen vor und beeinflussen, wie Gene in Proteine übersetzt werden. Bisher fehlte der Forschung jedoch eine einheitliche Methode, um ihre Aktivität zu messen.
Das Team entwickelte ein Werkzeugset, das zirkuläre RNA-Reporter mit fortschrittlichen Färbetechniken für einzelne mRNA-Moleküle kombiniert. Dieser Ansatz ermöglicht eine präzise Verfolgung der IRES-Funktion – sowohl in kultivierten Zellen als auch in embryonalem Gewebe. Dabei zeigte sich, dass das Ribosom selbst aktiv die Genexpression während der Proteinsynthese reguliert, was das Verständnis der Translationskontrolle um eine neue Ebene erweitert.
Die Studie, gefördert von der Deutschen Forschungsgemeinschaft (DFG) und der Universität Bonn, wurde am 13. März 2025 in The EMBO Journal veröffentlicht. Ein Patent für nicht-virale IRES-Sequenzen, die die Translation zirkulärer RNA verbessern sollen, liegt gemeinsam beim UKB, der Universität Bonn und der Stanford University.
Das Werkzeugset setzt einen neuen Maßstab für die Erforschung von IRES und bietet Forscher:innen eine zuverlässigere Methode, um diese Sequenzen zu charakterisieren. Die Erkenntnisse könnten das Verständnis der Genregulation vertiefen und zukünftige Entwicklungen in Biotechnologie und Medizin vorantreiben. Die Studie ist unter folgender DOI abrufbar: https://doi.org/10.1038/s44318-025-00404-5.